MIKROBIELLE FORENSIK: EINE LEISTUNGSSTARKE DISZIPLIN ZUR AUFKLÄRUNG UNGEWÖHNLICHER BIOLOGISCHER EREIGNISSE
Microbial Forensics: A powerful Discipline for the Medical Reconnaissance of Unusual Biological Events
Aus dem Institut für Mikrobiologie der Bundeswehr, München (Leiter: Oberstarzt Prof. Dr. L. Zöller)
Holger C. Scholz und Lothar Zöller
Biologische Bedrohungen sind gegenwärtig eher mit asymmetrischen Kriegsszenarien und nichtstaatlichen Akteuren assoziiert als mit staatlich organisierten Fähigkeiten des Einsatzes biologischer Waffen. In solchen Szenarien wird aber die absichtliche Freisetzung biologischer (B-) Agenzien wahrscheinlich zunächst unentdeckt bleiben, bis ein Cluster von Krankheitsfällen auf ein ungewöhnliches Ausbruchsgeschehen hinweist.
Hauptziele der medizinischen B-Aufklärung sind dann die Identifizierung des auslösenden Agens, die Ermittlung der Infektionsquelle sowie die Unterscheidung zwischen einem natürlichen und einem artifiziellen Geschehen. Im Gegensatz zur Untersuchung natürlicher Ausbruchsgeschehen müssen im Falle ungewöhnlicher Ereignisse forensische Aspekte von Anfang an in Betracht gezogen und implementiert werden. Bei der dann zum Einsatz kommenden „Mikrobiellen Forensik“ handelt es sich um eine neue Wissenschaftsdisziplin. Mithilfe genetischer Typisierungstechniken wird ein „genetischer Fingerabdruck“ des speziellen Ausbruch- Stammes erstellt und mit in Datenbanken gespeicherten Referenzprofilen verglichen. Dadurch wird der Untersucher im Idealfall in die Lage versetzt, den Stamm zu identifizieren und Aussagen zu seiner Herkunft zu machen.
Der Übersichtsbeitrag unterstreicht die Wichtigkeit der mikrobiellen Forensik bei der Aufklärung ungewöhnlicher biologischer Ereignisse und schildert die im Bereich des medizinischen B-Schutzes bereits aufgebauten Fähigkeiten sowie die Herausforderungen für die weitere Entwicklung.
Dazu wurde am Institut für Mikrobiologie der Bundeswehr eine Vielzahl molekularer Typisierungsmethoden etabliert, um die genetischen Unterschiede zwischen verschiedenen Erreger-Stämmen zu detektieren. Die Typisierungsdaten von mehreren Hundert Stämmen verschiedener Spezies wurden in einer Datenbank (BioNumerics) erfasst.
Schlussfolgerungen:
Die größten Herausforderungen bei der Weiterentwicklung bestehen darin, umfassende und supranational verfügbare Datenbanken mit international standardisierten Typisierungsdaten zu erstellen und bei den Typisierungsverfahren ein Qualitätsmanagement zu implementieren.
Summary
Biothreats are currently associated with asymmetric warfare scenarios and non-state actors rather than with state-run bio-warfare facilities. In such scenarios, the deliberate release of a biological agent will most probably remain undetected until a cluster of cases will suggest an unusual outbreak of disease. Major goals of medical bio reconnaissance are rapidly to identify the causative agent, to trace the source and to differentiate between natural and deliberate outbreaks. In contrast to the investigation of overt natural outbreaks, forensic aspects have to be considered and implemented quite from the beginning when unusual outbreaks are to be investigated. If a biothreat agent is detected, it may be necessary to implement microbial forensics, a relatively new discipline that is mainly concerned with taking molecular fingerprints of biothreat agents by means of sophisticated molecular typing techniques. Its objective is to identify and trace back a particular strain by comparing it with the reference fingerprints stored in a typing database.
This overview underscores the importance of microbial forensics for the reconnaissance of unusual biological events, describes the respective capabilities that already have been developed in the Bundeswehr and outlines the challenges towards further developments. A broad spectrum of sophisticated typing techniques has been established in the Bundeswehr Institute of Microbiology. The typing data of several hundred strains of various species was fed into the BioNumerics database.
Conclusions:
In the near future, the major challenges in microbial forensics will be the development of large databases with internationally standardized typing data and the implementation of quality management.
Einleitung
Die heutige Risikoeinschätzung für Anschläge mit biologischen (B-)Agenzien gegen militärische Einrichtungen oder Operationen geht nicht mehr primär von den für die früheren staatlichen BWaffen- Programme typischen Ausbringungsmitteln (Gefechtsköpfe, Flugzeuge) aus. Vielmehr sind Szenarien wahrscheinlicher, bei denen die Ausbringung des Agens durch Terrorgruppen mit einfachen beziehungsweise behelfsmäßigen Vorrichtungen erfolgt. Solche Anschläge haben eine geringe Chance, schon im Moment der Freisetzung des Agens entdeckt zu werden. Vielmehr wird der Sanitätsdienst zunächst mit einem Cluster von Krankheitsfällen konfrontiert werden. In einer solchen Situation kommt es zunächst darauf an, Ausbruchsmerkmale zu identifizieren, die das Geschehen als „ungewöhnlich“ qualifizieren. Bei einem ungewöhnlichen Ausbruch ist die Möglichkeit einer absichtlichen Herbeiführung durch Freisetzung eines biologischen Agens in Betracht zu ziehen. In einem solchen Szenario ist die frühzeitige Diagnosestellung entscheidend, um die Infektketten zu unterbrechen und die Zahl schwerer und letaler Verläufe zu begrenzen. Zugleich sind beim diagnostischen Vorgehen und bei der Ausbruchsaufklärung von Anbeginn an forensische Aspekte zu berücksichtigen, die im Falle des Nachweises eines B-Agens im Hinblick auf die möglichen politischen und militärischen Konsequenzen eine auch im Sinne einer belastbaren Beweisführung zweifelsfreie Diagnose ermöglichen. Dazu gehört zum Beispiel die Wahrung einer lückenlosen „Chain of Custody“, somit der Ausschluss von Verwechslungen oder Manipulationen von Proben. Dies gilt für menschliche Untersuchungsmaterialien in gleicher Weise wie für tierische Proben, Lebensmittel-, Trinkwasser- oder Umweltproben, die im Rahmen der Ausbruchsaufklärung benötigt werden. Da die meisten potenziellen B-Agenzien auch als natürliche Erreger von Infektionen vorkommen, ist im weiteren Verlauf eine Aussage zu treffen, ob es sich um eine natürliche oder absichtlich herbeigeführte Erkrankung handelt. Hierzu werden auch neue molekulare Differenzierungsmethoden eingesetzt, die unter dem Begriff „mikrobielle Forensik“ oder auch „Bioforensik“ eine neue Disziplin in der B-Aufklärung begründet haben.
Perzeption biologischer Risiken und Bedrohungen
Seit Inkrafttreten der Konvention über das Verbot der Entwicklung, Herstellung und Lagerung bakteriologischer (biologischer) Waffen und Toxinwaffen (B-Waffen-Übereinkommen) im März 1975 ist die Herstellung und Lagerung von Waffen auf der Basis von Mikroorganismen sowie anderen biologischen Substanzen oder Toxinen verboten. Der Vertrag wurde bisher von 164 Staaten ratifiziert, darunter durch die USA, Russland, Großbritannien, Deutschland, Frankreich und die Volksrepublik China.
Die Risikoperzeption für biologische Gefahren nahm daraufhin im Westen stark ab. Technisch-wissenschaftlich versierte Kräfte wurden entlassen, Aufklärungs- Institutionen geschlossen und die Budgets drastisch gekürzt. Das Augenmerk richtete sich fortan mehr auf die Bedrohung durch atomare Waffen. Erst das Bekanntwerden des in der früheren Sowjetunion heimlich weitergeführten und sogar ausgebauten staatlichen B-Waffen-Programms und das durch einen Überläufer verratene BWaffen- Programm des Irak führten erneut zu einer verstärkten Risikoperzeption. Nach den Milzbrand-Anschlägen von 2001 in den USA rückten die biologischen Risiken endgültig wieder in den Fokus staatlicher Gegenmaßnahmen. Auf diese Art von Anschlägen waren die USA nur unzureichend vorbereitet. Getriggert durch die dramatischen Ereignisse vom September 2001 wurde daraufhin ein umfassendes Konzept zur Überwachung, Erkennung und Abwehr biologischer Gefahren entwickelt und die Forschung und Entwicklung im biologischen Schutz mit hohem finanziellem Aufwand forciert. In diesem Rahmen wurde auch erstmals die „Mikrobielle Forensik“ etabliert.
Die von biologischen Agenzien ausgehenden Risiken sind heute hauptsächlich mit kriminellen (Biocrime) oder terroristischen (Bioterrorismus) Aktivitäten assoziiert. Eine reale Bedrohungslage ergibt sich aus dem nachrichtendienstlich identifizierten Interesse von bestimmten Personengruppen an biologischen Kampfstoffen und aus diesbezüglich festgestellten Einzelereignissen. Über fortbestehende staatliche B-Waffen- Programme gibt es nach der Beseitigung des Saddam-Regimes im Irak und dem Untergang der ehemaligen Sowjetunion keine validen Erkenntnisse.
Beispiele aufgedeckter bioterroristischer und krimineller Aktivitäten sind unter anderem:
- Kontamination von Salat-Bars mit Salmonellen durch die politisch-religiös motivierte Rajneeshee-Kommune (1),
- vorgetäuschte Anthrax-Anschläge in den späten 90igern in den USA (2) und nach 2001 auch in Deutschland,
- Versuche der Aum Shinrikyo-Sekte in Japan, Botulinumtoxin, Milzbrandsporen, Vibrio cholerae (Erreger der Cholera) und Q-Fieber-Erreger (Coxiella burnetii) zu bioterroristischen Zwecken einzusetzen (3),
- Tötung eines bulgarischen Dissidenten mithilfe des Pflanzengifts Ricin und
- Briefattentate von 2001 mit Anthrax- Sporen in den USA.
Daneben gab es weitere dokumentierte, aber nicht erfolgreiche Anschläge.
Mikrobielle Forensik
Klassische forensische Methoden wie die Auswertung von Fingerabdrücken oder die ballistische Analyse von Projektilen sind seit Jahrzehnten fester Bestandteil der kriminalistischen Verbrechensaufklärung. Seit der Erfindung hochspezifischer molekularer Methoden zur Analyse der Erbinformation von Tätern (DNA-Analyse) in den 90iger Jahren liefern forensische DNAUntersuchungen, zum Beispiel von Hautschuppen, Haaren, etc., einen wichtigen zusätzlichen Beitrag zur Verbrechensbekämpfung. Durch retrospektive Analysen geeigneter Materialien können selbst Morde aufgeklärt werden, die mitunter 30 Jahre zurückliegen, aber mangels schlüssiger Beweise bisher nicht aufgeklärt werden konnten. Analog zur Analyse von Fingerabdrücken kann auch eine Übereinstimmung des DNA-Profils („genetischer Fingerabdruck“) mit einem in einer Datenbank hinterlegten Profil zur eindeutigen Täteridentifizierung führen.
Was aber, wenn die Tat nicht mit konventionellen Tatwerkzeugen oder Waffen begangen wurde, sondern mit einem lebenden hochpathogenen Mikroorganismus, der darauf abzielt, möglichst viele Menschen zu infizieren, die daraufhin schwer erkranken oder sterben? Kann der ausgebrachte Mikroorganismus Hinweise auf seine Herkunft liefern oder sogar helfen, denjenigen zu identifizieren, der ihn absichtlich freigesetzt hat?
Die Wissenschaft, die sich die Beantwortung dieser Fragestellung zum Ziel gesetzt hat, heißt „Mikrobielle Forensik“ oder auch „Bioforensik“.
Moderne DNA-basierte Typisierungsmethoden ermöglichen die Erstellung von genetischen Fingerabdrücken der Mikroorganismen. Sie erlauben durch Vergleich der Profile eine Identifizierung von B-Agenzien unterhalb der Spezies- Ebene, das heißt auf der Stamm- oder sogar Isolat-Ebene. Solche Techniken wie die Pulsfeldgelelektrophorese (PFGE) werden seit Jahren genutzt, um Krankheitsausbrüche zu analysieren und die Verbreitung eines Erregers während eines Ausbruchs zu verfolgen. Diese Wissenschaftsdisziplin wird Molekulare Epidemiologie genannt.
Erst im Jahr 2010 hat das Beispiel des EHEC/HUS-Ausbruchs in Deutschland den Wert molekularer epidemiologischer Methoden für die Ausbruchsaufklärung gezeigt. Seit einigen Jahren existieren dynamische Typisierungsdatenbanken für diverse Krankenhausund Lebensmittelkeime wie zum Beispiel das Überwachungsprogramm „PulseNet“ der CDC in Atlanta (USA). Bei Bedarf können die hinterlegten genetischen Fingerprints abgerufen und mit den eigenen Daten eines aktuellen Ausbruchsgeschehens abgeglichen werden. Seit wenigen Jahren ist es außerdem möglich, in kürzester Zeit die vollständige Erbinformation eines Mikroorganismus zu bestimmen und zu analysieren. So ist es kürzlich im Rahmen des zitierten EHEC/HUS-Ausbruchs gelungen, durch die Anwendung der Next-Generation-Sequencing- (NGS)-Technologie die Erbinformation des Erregers zu ermitteln und durch Vergleich mit der Erbinformation bekannter EHEC-Stämme die Herkunft genauer zu definieren. Die mikrobielle Forensik unterscheidet sich von der molekularen Epidemiologie insoweit, als die gewonnenen erregerspezifischen Daten nicht nur wissenschaftlich akkurat, sondern auch in einer Form abgesichert sein müssen, dass sie Beweischarakter haben. Voraussetzung dafür ist, dass die Daten unter Beachtung strenger Qualitätsmanagement-Kriterien generiert wurden. Dies gilt für Probennahme und -versand ebenso wie für die Analytik selbst.
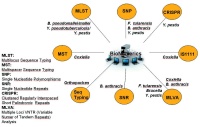
Abb 1: Molekulare Typisierungsverfahren und Datenbank im Überblick.
Typisierungsmethoden und Datenbanken
Zu den Laboranalysen, die in der mikrobiellen Forensik genutzt werden, gehören die Anzüchtung des Erregers, eine Reihe phänotypischer Analysen wie die Biochemie, Massenspektroskopie und Elektronenmikroskopie (zum Beispiel zur Feststellung von Zusätzen oder der Art der Zubereitung aerosolisierbarer Präparationen). Den Kern bilden aber Nukleinsäure-basierte Typisierungsmethoden, mit denen in definierten variablen Genabschnitten der Erregergenome Unterschiede in der Basenzusammensetzung festgestellt werden. Wie Menschen sich genetisch unterscheiden, so finden sich auch genetische Unterschiede zwischen verschiedenen Stämmen der gleichen Bakterien- oder Virusspezies. Je nachdem, wie fein die Methode differenziert, kann man genetische Unterschiede nicht nur zwischen Stämmen, sondern auch zwischen einzelnen Isolaten des gleichen Stammes nachweisen. Gängige Methoden sind zum Beispiel das Multilocus-Sequence-Typing (MLST) (4), die Multilocus-Variable-Number-of-Tandem- Repeat-Analyse (MLVA) (5) oder die Analyse von Single Nucleotide Polymorphisms (SNPs), Clustered Regularly Interspaced Short Palindromic Repeats (CRISPR) (6) sowie Genomsequenzierungen (7) und Microarrays.
Die Verfahren besitzen allerdings eine unterschiedliche Differenzierungstiefe. Goldstandard für Ausbruchsuntersuchungen ist derzeit die hochauflösende MLVA. Die genannten Methoden sind außerdem für die verschiedenen Erregerspezies unterschiedlich gut geeignet. Daher wird für jede Spezies ein eigenes Methodenspektrum eingesetzt, das auch auf jeweils spezifisch bei dieser Art vorkommende Genloci ausgerichtet ist (Abb 1).
Die Zukunft der molekularen Typisierung zeichnet sich schon ab. In den USA sind die Kosten für eine Gesamtgenomsequenzierung bereits auf unter 200 USD gefallen. Auch in Europa werden die Kosten entsprechend sinken. Auf dem in den USA erreichten Preisniveau wird die Gesamtgenomsequenzierung die bisher gebräuchlichen Methoden weitgehend ersetzen. Der Vergleich verschiedener Genome wird dann in erster Linie am Computer durch In-Silico-Analysen stattfinden, wobei durchaus die Kriterien der bisher verwendeten Typisierungsmethoden noch genutzt werden können.
Die Etablierung einer globalen und umfassenden Typisierungs-Referenzdatenbank nimmt eine Schlüsselposition bei der erfolgreichen Entwicklung der mikrobiellen Forensik ein. Dort werden nicht nur genetische Typisierungsinformationen, sondern auch weitere Informationen über die einzelnen Genotypen wie geografisches Vorkommen der Stämme, Herkunft oder Verbreitung in Laboratorien hinterlegt. Um einen Ausbruchsstamm zuordnen und mit Erfolgswahrscheinlichkeit identifizieren zu können, muss eine repräsentative Vielfalt aller genetischen Varianten einer Spezies hinterlegt sein. Voraussetzung für die Etablierung solcher Datenbanken ist der internationale Austausch von Daten, Methoden, lebenden Erregern und DNA zwischen Forschungseinrichtungen. Eine weitere Voraussetzung ist die Standardisierung der verwendeten Analysemethoden. Gegenwärtig sind viele Datensätze der einzelnen Länder untereinander inkompatibel, da mit unterschiedlichen Methoden erarbeitet. Es wird also in Zukunft ein wesentliches Ziel der mikrobiellen Forensik sein, die Methoden anzugleichen und einheitliche Analysealgorithmen zu entwickeln.
Die Erstellung einer internationalen Datenbank ist demnach nicht nur eine technische, sondern zugleich auch eine politische Herausforderung für die internationale Gemeinschaft, um den freien Austausch der benötigten Daten und Materialien zu ermöglichen. Dabei kommt der Kommunikation zwischen Wissenschaftlern, politischen Interessenvertretern sowie Bundesbehörden eine entscheidende Rolle zu. Naturgemäß stehen allerdings mögliche Dual-Use-Aspekte dem freien Austausch von Stämmen und Informationen entgegen. Es ist daher erforderlich, Regeln und Kontrollen zu implementieren, ohne aber unnötige Hindernisse aufzubauen.
Aus dieser Sicht ist die mikrobielle Forensik eine neue Wissenschaft, die sich zweckorientiert verschiedener bereits etablierter Methoden und Wissenschaften bedient. Dazu gehören mikrobielle Gen- und Genomanalysen, phylogenetische Untersuchungen, die klassische Forensik, die Bioinformatik, die Computerwissenschaften sowie die traditionelle Mikrobiologie und Epidemiologie.
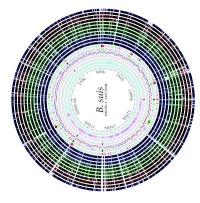
Abb 2: Zoombarer Genomatlas: Vergleichende Genomanalyse verschiedener Brucella-Arten.
Aufbau von Fähigkeiten der mikrobiellen Forensik im Medizinischen B-Schutz
In Zusammenarbeit mit nationalen und internationalen Typisierungsexperten wurden am Institut für Mikrobiologie der Bundeswehr (InstMikroBioBw) in den vergangenen Jahren verschiedene molekulare Typisierungsmethoden für B-Schutz-relevante Erreger wie Bacillus anthracis, Yersinia pestis, Francisella tularensis, Brucella spp. und Burkholderia mallei/pseudomallei etc. etabliert. Zum Methodenspektrum (Abb 1) gehören moderne Analyseverfahren wie das oben erwähnte MLST, die MLVA, die SNP-Analyse bis hin zu Hochdurchsatz- Sequenziermethoden der nächsten Generation wie die 454 Pyrosequenziertechnologie (Roche Diagnostics) oder die Illumina-Sequenziertechnologie. Neu entwickelte Software ermöglicht es, zoombare Genomatlanten zur direkten Visualisierung von Sequenzunterschieden und für vergleichende Analysen auf Genomebene zu erstellen (Abb 2).
Das InstMikroBioBw verfügt über eine der umfassendsten Stammsammlungen human- und tierpathogener Mikroorganismen in Europa. Seit Ende der 80iger Jahre wurde die Stammsammlung ständig erweitert und umfasst heute mehrere Tausend Bakterien- und Virus- Isolate. Diese besonders wertvolle Stammsammlung ist eine Grundvoraussetzung, um neue Analyseverfahren zu entwickeln und zu validieren. Zudem macht die Stammsammlung das Institut zu einem gefragten und leistungsfähigen Kooperationspartner.
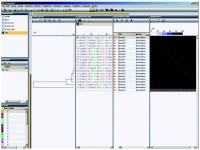
Durch Anwendung der oben gelisteten Typisierungsmethoden auf die Stammsammlung des Instituts konnten bereits von einer Vielzahl B-Schutz-relevanter Erreger genetische Profile erstellt und in einer Datenbank hinterlegt werden (Tab 1). Als Datenbankplattform dient die komplexe Analysesoftware BioNumerics (Applied Maths, Belgien) (Abb 3). Durch die Integration aller essenziellen bioinformatischen Analysetools, von einfachen Sequenzanalysen über komplexe Cluster-Analysen bis hin zur de-novo-Assemblierung ganzer Genomsequenzen stellt BioNumerics das ideale Analyse- und Auswertetool dar. Die Netzwerkfähigkeit erlaubt zudem einen raschen und unkomplizierten Datenaustausch zwischen einzelnen Projektpartnern.
Tab 1: Überblick über die am InstMikroBioBw bereits typisierten Erreger.
Um das InstMikroBioBw als einen leistungsfähigen und kompetenten Partner auf dem Feld der molekularen Erregertypisierung/ Bioforensik im europäischen Verbund zu positionieren, wurde 2010 eine permanente Arbeitsgruppe „Molekulare Typisierung und Bioforensik“ unter der Leitung von Priv.-Doz. Dr. Holger Scholz eingerichtet. Vorrangiges Ziel ist der Ausbau der internationalen Vernetzung des Instituts mit weiteren Institutionen, die auf dem Gebiet tätig sind. Auf europäischer Ebene ist das Institut als wichtiger Partner im European Biodefense Laboratory Network (EBLN) der European Defence Agency (EDA) vertreten. Ziel des Gemeinschaftsprojekts von 12 Ländern ist es, Analyseverfahren zu harmonisieren und zu standardisieren sowie eine gemeinsam nutzbare Datenbank für BSchutz- relevante Erreger aufzubauen. Durch die Bündelung der Ressourcen und die enge Zusammenarbeit verschiedener Länder sollen die europäischen Fähigkeiten im Bereich des medizinischen B-Schutzes verbessert werden. Auf transatlantischer Ebene existiert eine Kooperation mit der Arbeitsgruppe von Prof. Dr. Paul Keim an der Northern Arizona University, Flagstaff, Arizona. Paul Keim ist einer der führenden Spezialisten auf dem Gebiet der molekularen Typisierung und Bioforensik in den USA und war maßgeblich an den Untersuchungen der Briefattentate mit Sporen von Bacillus anthracis im Jahre 2001 beteiligt. In einem seit 2010 vom Department of Homeland Security (DHS) geförderten Projekt „Technology and Data Integration with the Bundeswehr Institute of Microbiology“ sollen Typisierungsmethoden angeglichen und eine gemeinsame Datenbank etabliert werden.
Eine weitere Kooperation zur umfassenden Typisierung von Yersinia pestis, dem Erreger der Pest, besteht mit dem National Center of Infectious Diseases Natural Foci (NCIDNF), Ulan Bator, Mongolei. Die Typisierung mongolischer Peststämme ist einzigartig und liefert neue Erkenntnisse zur Evolution dieses aus Sicht des Medizinischen BSchutzes wichtigen Erregers (8, 9).
Abb 3: BioNumerics Datenbank- und Analysesoftware (Applied Maths) als gemeinsame Datenbankplattform.
Schlussfolgerungen und Ausblick
Während in Europa eine gemeinsame Strategie fehlt, um den biologischen Risiken entgegenzuwirken, und die mikrobielle Forensik noch in den Kinderschuhen steckt, ist dies in den USA anders. In eindrucksvoller Weise wird im Report zur Nationalen Forschungs- und Entwicklungsstrategie zur Mikrobiellen Forensik ein Konzept zur bioterroristischen Gefahrenabwehr vorgestellt. Zweck dieser Nationalen Strategie ist es, die Forschungsanstrengungen der US-Regierung zur Förderung der mikrobiellen Forensik zu lenken und zu bündeln, um den Vereinigten Staaten bei einem potenziellen oder tatsächlichen biologischen Anschlag eine wissenschaftlich optimal abgesicherte Fähigkeit zur Unterstützung von Zuordnungsermittlungen an die Hand zu geben. Diese Strategie beinhaltet eine Forschungsagenda für die Bioforensik und zielt darüber hinaus auf die Förderung von behördenübergreifender Koordination und die Schulung von Entscheidungsträgern sowie von wissenschaftlichem und technischem Personal auf diesem Gebiet ab.
Beindruckend sind auch die US-Investitionen in die Forschungsinfrastruktur. So wurde kurz nach den Anthrax-Anschlägen der Bau des National Bioforensic Analysis Center (NBFAC) für 143 Mio. USD initiiert, das zusammen mit einem weiteren Institut, dem National Biological Threat Characterization Center (NBTCC) gezielt Fragen der mikrobiellen Forensik bearbeitet. Das NBFAC verfügt im Vollbetrieb über 150 Mitarbeiter mit einem jährlichen Budget von 50 Mio. US-Dollar. Ein ähnlicher Ansatz wäre auf europäischer Ebene wünschenswert. Allerdings sind staatliche Investitionen in den genannten Größenordnungen hier kaum zu erwarten. Der Aufbau einer Bioforensik kann daher nur gelingen, wenn die auf dem Gebiet des B-Schutzes tätigen militärischen und zivilen Institutionen sich zu einem B-Schutz-Netzwerk zusammenschlie ßen. Sie müssen ihre Methoden standardisieren und durch Implementierung eines Qualitätsmanagements die genetische Typisierung von Mikroorganismen zur Forensik weiterentwickeln. Auch alle Bereiche des Gesundheitswesens, die Aufgaben in der Ausbruchsaufklärung und Biogefahrenabwehr wahrnehmen, sind dabei gefordert, denn im Mittelpunkt der wahrscheinlichen Szenarien werden Patienten stehen. Das Institut für Mikrobiologie der Bundeswehr kann dazu wertvolle Beiträge leisten und hat in Deutschland bereits das am weitesten entwickelte Methodenrepertoire. Umfassende staatliche Forschungsförderprogramme sollten dieser Problematik gewidmet werden.
Literatur
- Torok TJ, Tauxe RV, Wise RP, et al.: A large community outbreak of salmonellosis caused by intentional contamination of restaurant salad bars. JAMA 1997; 278: 389-395.
- Moran GJ: Update on emerging infections from the Centers for Disease Control and Prevention: bioterrorism alleging use of anthrax and interim guidelines for management- United States, 1998. Ann Emerg Med 1999; 34: 229-232.
- Olson KB: Aum Shinrikyo: once and future threat? Emerg Infect Dis 1999; 5: 513- 516.
- Schouls LM, Reulen S, Duim B, et al.: Comparative genotyping of Campylobacter jejuni by amplified fragment length polymorphism, multilocus sequence typing, and short repeat sequencing: strain diversity, host range, and recombination. J Clin Microbiol 2003; 41: 15-26.
- Marsh JW, O’Leary MM, Shutt KA, et al.: Multilocus variable-number tandem-repeat analysis for investigation of Clostridium difficile transmission in Hospitals. J Clin Microbiol 2006; 44: 2558-2566.
- Pourcel C, Salvignol G, Vergnaud G: CRISPR elements in Yersinia pestis acquire new repeats by preferential uptake of bacteriophage DNA, and provide additional tools for evolutionary studies. Microbiology 2005; 151: 653-663.
- Read TD, Salzberg SL, Pop M, ,et al.: Comparative genome sequencing for discovery of novel polymorphisms in Bacillus anthracis. Science 2002; 296: 2028- 2033.
- Kiefer D, Dalantai G, Damdindorj T, et al.: Phenotypical Characterization of Mongolian Yersinia pestis Strains. Vector Borne Zoonotic Dis. 2011; Oct 24. [Epub ahead of print]
- Riehm JM, Vergnaud G, Kiefer D, et al.: Yersinia pestis Lineages in Mongolia. PLoS One. 2012; 7(2):e30624.
Datum: 27.08.2012
Quelle: Wehrmedizinische Monatsschrift 2012/4